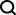Technologie-Peripheriegeräte
Technologie-Peripheriegeräte
 KI
KI
 Mit einer 36-mal höheren Auflösung als die ursprüngliche Auflösung nutzten Teams der Beihang-Universität und der Tsinghua-Universität KI, um Gewebe mit hoher Auflösung auf einer Multi-Space-Omics-Plattform zu charakterisieren, veröffentlicht im Nature-Unterjournal
Mit einer 36-mal höheren Auflösung als die ursprüngliche Auflösung nutzten Teams der Beihang-Universität und der Tsinghua-Universität KI, um Gewebe mit hoher Auflösung auf einer Multi-Space-Omics-Plattform zu charakterisieren, veröffentlicht im Nature-Unterjournal
Mit einer 36-mal höheren Auflösung als die ursprüngliche Auflösung nutzten Teams der Beihang-Universität und der Tsinghua-Universität KI, um Gewebe mit hoher Auflösung auf einer Multi-Space-Omics-Plattform zu charakterisieren, veröffentlicht im Nature-Unterjournal

1. Einführung
Spatial Omics hat den Umfang der molekularen Klassenanalyse erweitert, aber viele Techniken sind durch die räumliche Auflösung begrenzt. Bestehende Berechnungsmethoden zielen hauptsächlich auf transkriptomische Daten ab und sind nicht an neue räumliche Omics-Technologien anpassbar.
2. soScope-Framework
Forscher der Beihang-Universität und der Tsinghua-Universität schlugen soScope vor, ein einheitliches Generations-Framework, das die Qualität und Auflösung räumlicher Omics-Daten verbessern soll.
3. Technisches Prinzip
soScope fasst multimodale Gewebeinformationen aus Omics, räumlichen Beziehungen und Bildern zusammen. Geben Sie Omics-Spektren mit verbesserter Auflösung durch gemeinsame Inferenz von Verteilungsprioritäten und Omics-spezifischer Modellierung aus.
4. Leistungsbewertung
soScopes Bewertungsergebnisse für Visium, die Feinstruktur des embryonalen Herzens
- Korrigiert um Proben- und technische Verzerrungen
- 5. Erweiterte Anwendungen
6. Fazit
soScope bietet ein vielseitiges Tool, das die Nutzung räumlicher Omics-Technologie und -Ressourcen verbessert.7. Referenz
Diese Forschung wurde am 2. August 2024 in „Nature Communications“ unter dem Titel „Gewebecharakterisierung mit erhöhter Auflösung über räumliche Omics-Plattformen mit tiefem generativem Modell“ veröffentlicht.Gewebe-Raum-Omics-Technologie
 Gewebe bestehen aus Zellen mit unterschiedlichen molekularen Zuständen und räumlichen Organisationen. Die räumliche Omics-Technologie hat in den letzten Jahren erhebliche Fortschritte gemacht und ermöglicht die räumliche Analyse verschiedener Molekülklassen unter Beibehaltung des räumlichen Kontexts.
Gewebe bestehen aus Zellen mit unterschiedlichen molekularen Zuständen und räumlichen Organisationen. Die räumliche Omics-Technologie hat in den letzten Jahren erhebliche Fortschritte gemacht und ermöglicht die räumliche Analyse verschiedener Molekülklassen unter Beibehaltung des räumlichen Kontexts.
Gefrorenes oder formalinfixiertes Gewebe kann den molekularen Zustand beeinflussen und die Sequenzierungsgenauigkeit verringern.
Die meisten Techniken haben eine begrenzte räumliche Auflösung, was es schwierig macht, subtile Heterogenitäten in der Gewebestruktur aufzudecken.
- Computertechnologie kann die Auflösung räumlicher Omics-Daten verbessern, aber die meisten aktuellen Methoden zielen nur auf eine einzige Gewebemodalität ab, was es schwierig macht, multimodale Informationen vollständig zu nutzen.
- soScope: Verbesserung der räumlichen Auflösung und Datenqualität
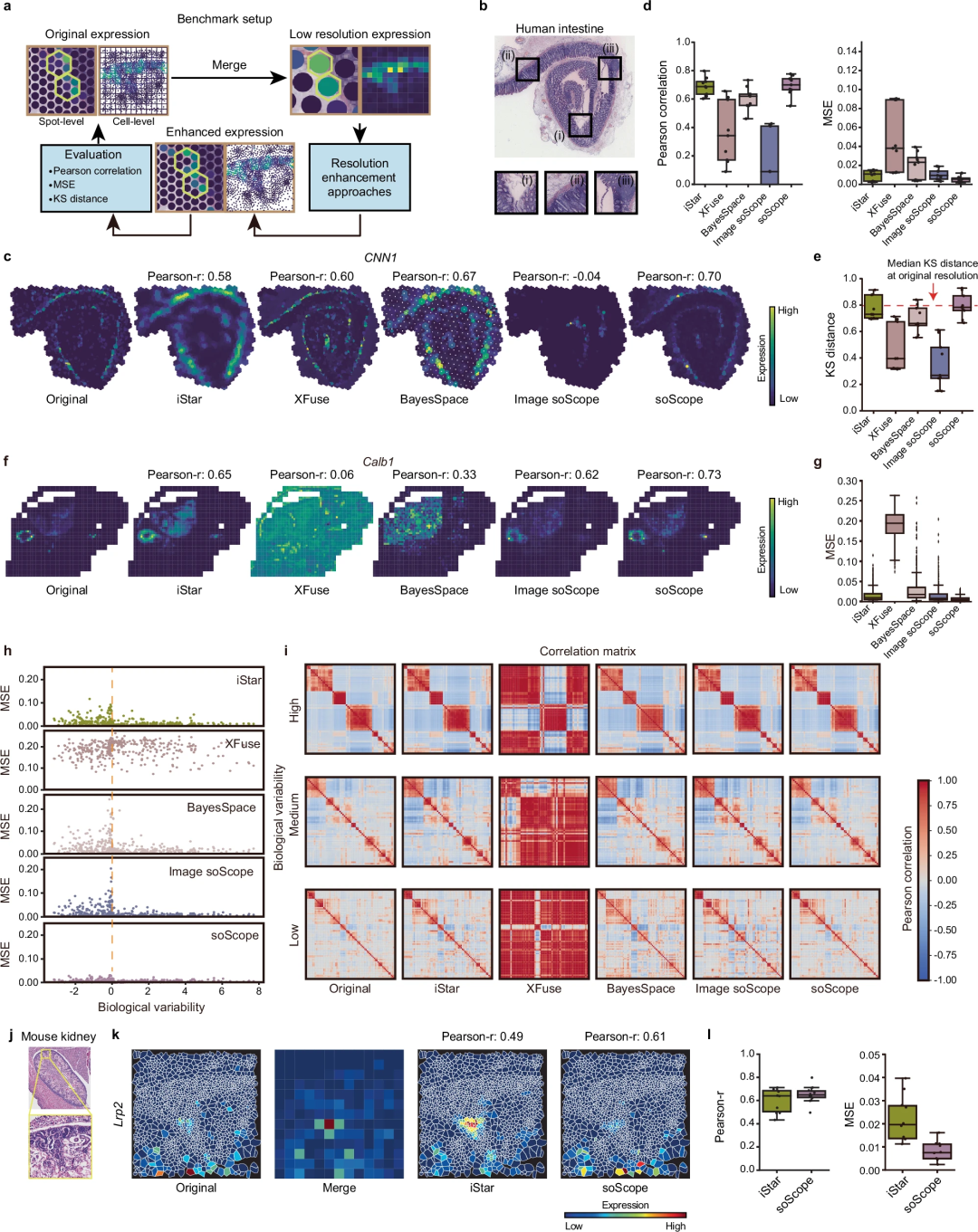
soScope behandelt jeden Punkt als eine Sammlung von „Unterpunkten“ mit verbesserter räumlicher Auflösung, deren Omics-Eigenschaften mit der räumlichen Lage und morphologischen Mustern zusammenhängen. SoScope verwendet dann ein multimodales Deep-Learning-Framework, um Spot-Omics-Profile, räumliche Beziehungen und hochauflösende Morphologiebilder zu integrieren und gemeinsam Omics-Profile mit Sub-Spot-Auflösung abzuleiten. Durch die Auswahl omics-spezifischer Verteilungen kann soScope die Variation verschiedener räumlicher Omics-Daten genau modellieren und reduzieren.
Abbildung:Überblick über soScope und seine Anwendungen. (Quelle: Papier)
Einheitliches Tool, kombiniert mit multimodalen Gewebekarten Verbesserte Omics-Karten (verschiedene Molekülklassen)
- Verbesserung der räumlichen Auflösung
- Reduzierung unnötiger Änderungen
- Charakterisierung Komplexes Gewebe Strukturen (bei nativer Auflösung nicht erkennbar)
- Abbildung: Auswertung von soScope anhand räumlicher Transkriptomik-Datensätze aus mehreren Geweben und Plattformen. (Quelle: Papier)
-
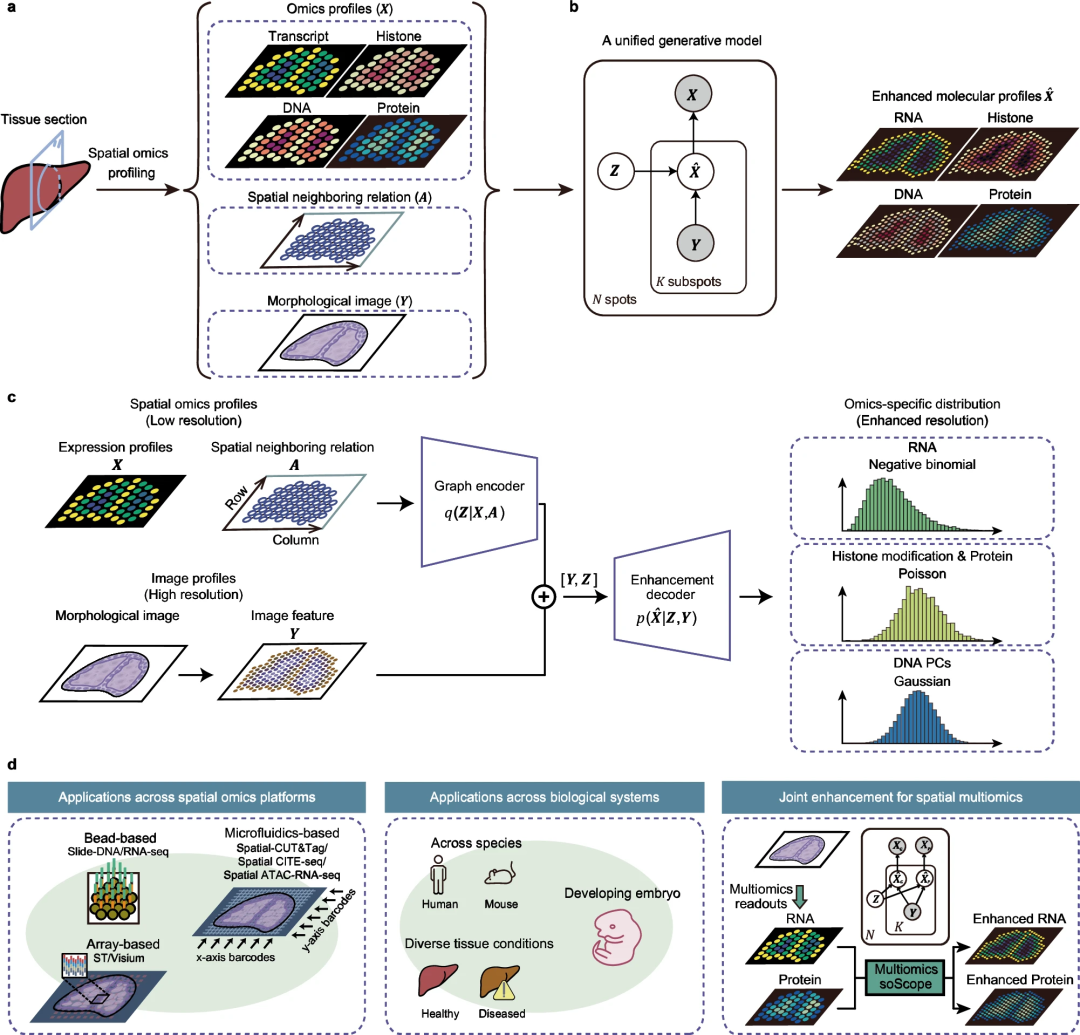
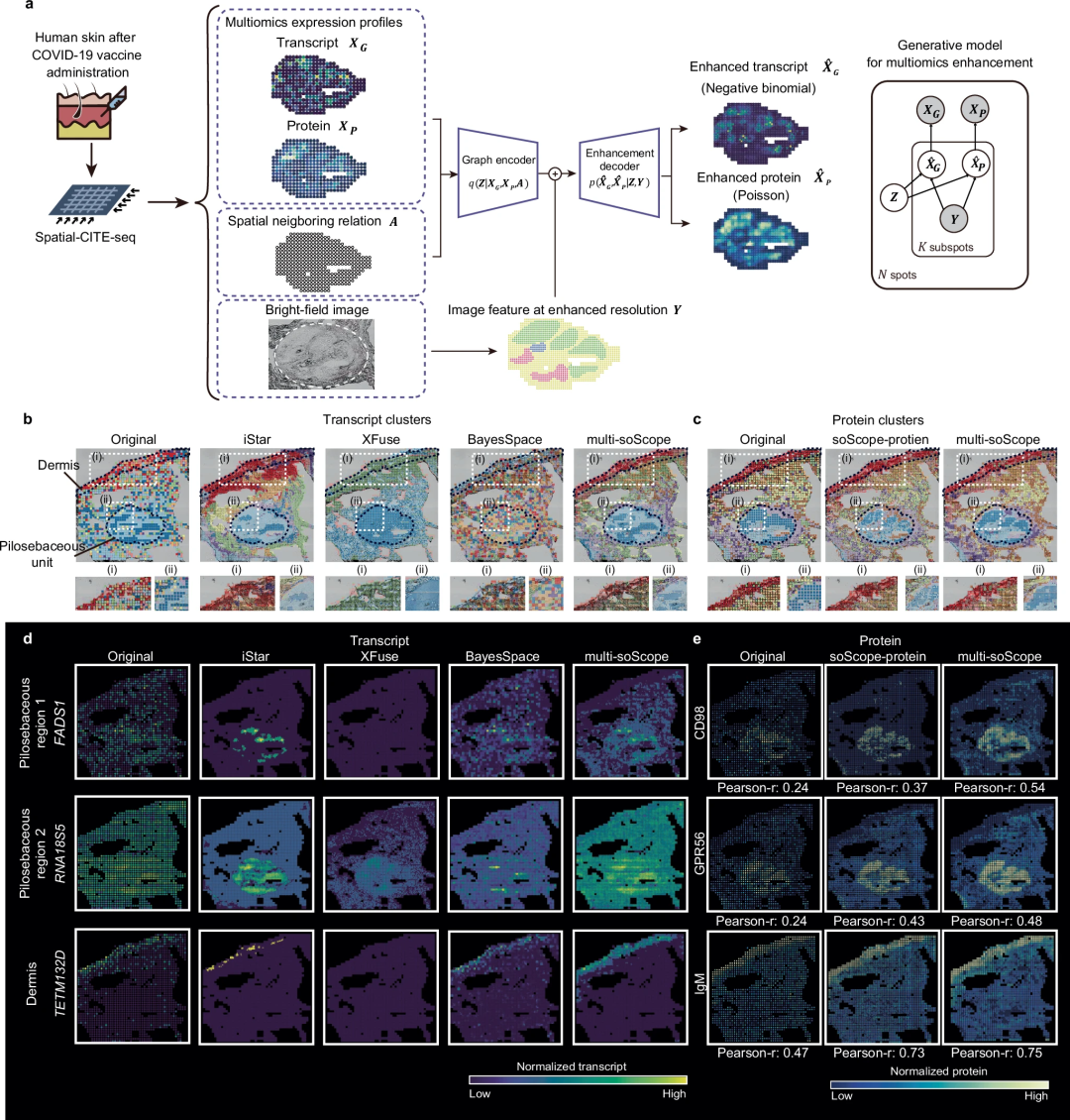
Das Team hat die Wirksamkeit und Generalisierbarkeit von soScope für mehrere Molekültypen, die mit mehreren räumlichen Techniken analysiert wurden, umfassend bewertet, darunter Visium, Xenium, Spatial-CUT&Tag, Slide-DNA-Seq, Slide-RNA-Seq, Spatial-CITE -seq und räumliche ATAC-RNA-seq.
In gesunden und erkrankten Geweben verbessert soScope die Identifizierung von Gewebedomänen, erhöht die Differenzierbarkeit bekannter Marker und korrigiert Daten und technische Verzerrungen. Die Methode ist in der Lage, feinere Gewebestrukturen mit einer bis zu 36-mal höheren Auflösung als die ursprüngliche Auflösung sichtbar zu machen. Es kann räumliche Multi-Omics-Daten effizient anpassen, um gleichzeitig Multi-Omics-Profile zu verbessern.
Forscher stellen fest, dass es mehrere bildbasierte räumliche Omics-Technologien wie seqFISH, STARmap und MERFISH gibt, die eine räumliche Analyse direkt mit Einzelzellauflösung durchführen können, allerdings auf Kosten eines geringeren Omics-Durchsatzes und kleinerer Gewebebereiche. Obwohl soScope erweiterte Profile für vorab festgelegte Subspot- oder Zellstandorte bereitstellt, erreicht es möglicherweise keine subzelluläre Auflösung.
Auflösung weiter verbessern:
- SoScope so ändern, dass gepaarte Einzelzell-Omics-Daten aus demselben Gewebe einbezogen werden, wodurch Informationen mit höherer Auflösung für die Unterpunktinferenz bereitgestellt werden.
- Integrieren Sie H&E-Bilder als Eingabe, die von menschlichen Experten in bestimmten klinischen Studien leicht mit Anmerkungen versehen werden können.
- Ändern Sie soScope, um menschliche Bezeichnungen zu integrieren und die hintere Schlussfolgerung auf halbüberwachte Weise zu steuern, wodurch die latente Darstellung und das Profillernen verbessert werden.
Rechenkosten reduzieren:
Bei größeren Datensätzen, die mehrere zusammenhängende Schichten desselben Organs enthalten, kann soScope:
- Auf Teildaten trainieren.
- Auf verbleibende Gewebeabschnitte auftragen.
Potenzial:
Mit der kontinuierlichen Erweiterung der räumlichen Omics-Datenressourcen und dem Aufkommen neuer räumlicher Technologien glauben Forscher, dass soScope das folgende Potenzial hat:
- Ein vielseitiges Werkzeug.
- Machen Sie räumliche Omics-Daten voll aus.
- Verbessern Sie das Verständnis der Wissenschaftler für komplexe Gewebestrukturen und biologische Prozesse.
Papierlink:
https://www.nature.com/articles/s41467-024-50837-5
Das obige ist der detaillierte Inhalt vonMit einer 36-mal höheren Auflösung als die ursprüngliche Auflösung nutzten Teams der Beihang-Universität und der Tsinghua-Universität KI, um Gewebe mit hoher Auflösung auf einer Multi-Space-Omics-Plattform zu charakterisieren, veröffentlicht im Nature-Unterjournal. Für weitere Informationen folgen Sie bitte anderen verwandten Artikeln auf der PHP chinesischen Website!

Heiße KI -Werkzeuge
Undresser.AI Undress
KI-gestützte App zum Erstellen realistischer Aktfotos
AI Clothes Remover
Online-KI-Tool zum Entfernen von Kleidung aus Fotos.

Undress AI Tool
Ausziehbilder kostenlos

Clothoff.io
KI-Kleiderentferner
Video Face Swap
Tauschen Sie Gesichter in jedem Video mühelos mit unserem völlig kostenlosen KI-Gesichtstausch-Tool aus!

Heißer Artikel

Heiße Werkzeuge

Notepad++7.3.1
Einfach zu bedienender und kostenloser Code-Editor

SublimeText3 chinesische Version
Chinesische Version, sehr einfach zu bedienen

Senden Sie Studio 13.0.1
Leistungsstarke integrierte PHP-Entwicklungsumgebung

Dreamweaver CS6
Visuelle Webentwicklungstools

SublimeText3 Mac-Version
Codebearbeitungssoftware auf Gottesniveau (SublimeText3)

Heiße Themen
 1667
1667
 14
14
 1426
1426
 52
52
 1328
1328
 25
25
 1273
1273
 29
29
 1255
1255
 24
24
 „Defect Spectrum' durchbricht die Grenzen der herkömmlichen Fehlererkennung und erreicht erstmals eine hochpräzise und umfassende semantische Fehlererkennung in der Industrie.
Jul 26, 2024 pm 05:38 PM
„Defect Spectrum' durchbricht die Grenzen der herkömmlichen Fehlererkennung und erreicht erstmals eine hochpräzise und umfassende semantische Fehlererkennung in der Industrie.
Jul 26, 2024 pm 05:38 PM
In der modernen Fertigung ist die genaue Fehlererkennung nicht nur der Schlüssel zur Sicherstellung der Produktqualität, sondern auch der Kern für die Verbesserung der Produktionseffizienz. Allerdings mangelt es vorhandenen Datensätzen zur Fehlererkennung häufig an der Genauigkeit und dem semantischen Reichtum, die für praktische Anwendungen erforderlich sind, was dazu führt, dass Modelle bestimmte Fehlerkategorien oder -orte nicht identifizieren können. Um dieses Problem zu lösen, hat ein Spitzenforschungsteam bestehend aus der Hong Kong University of Science and Technology Guangzhou und Simou Technology innovativ den „DefectSpectrum“-Datensatz entwickelt, der eine detaillierte und semantisch reichhaltige groß angelegte Annotation von Industriedefekten ermöglicht. Wie in Tabelle 1 gezeigt, bietet der Datensatz „DefectSpectrum“ im Vergleich zu anderen Industriedatensätzen die meisten Fehleranmerkungen (5438 Fehlerproben) und die detaillierteste Fehlerklassifizierung (125 Fehlerkategorien).
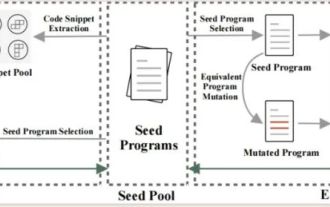 Die Tianjin-Universität und die Beihang-Universität sind maßgeblich am „Cangjie'-Projekt von Huawei beteiligt und haben das erste KI-Agent-Programmier-Framework „Cangqiong' auf Basis inländischer Programmiersprachen auf den Markt gebracht.
Jun 23, 2024 am 08:37 AM
Die Tianjin-Universität und die Beihang-Universität sind maßgeblich am „Cangjie'-Projekt von Huawei beteiligt und haben das erste KI-Agent-Programmier-Framework „Cangqiong' auf Basis inländischer Programmiersprachen auf den Markt gebracht.
Jun 23, 2024 am 08:37 AM
Laut Nachrichten dieser Website vom 22. Juni stellte Huawei gestern Entwicklern auf der ganzen Welt die von Huawei selbst entwickelte Programmiersprache Cangjie vor. Dies ist der erste öffentliche Auftritt der Programmiersprache Cangjie. Laut Anfragen auf dieser Website waren die Tianjin-Universität und die Pekinger Universität für Luft- und Raumfahrt stark an der Forschung und Entwicklung von Huaweis „Cangjie“ beteiligt. Tianjin-Universität: Cangjie-Programmiersprachen-Compiler Das Software-Engineering-Team der Abteilung für Intelligenz und Informatik der Tianjin-Universität hat sich mit dem Huawei Cangjie-Team zusammengetan, um sich intensiv an der Qualitätssicherungsforschung des Cangjie-Programmiersprachen-Compilers zu beteiligen. Berichten zufolge ist der Cangjie-Compiler die Basissoftware, die eine Symbiose mit der Programmiersprache Cangjie eingeht. In der Vorbereitungsphase der Cangjie-Programmiersprache wurde ein hochwertiger Compiler, der dazu passt, zu einem der Kernziele. Während sich die Programmiersprache Cangjie weiterentwickelt, wird der Cangjie-Compiler ständig aktualisiert und verbessert. In den letzten fünf Jahren an der Tianjin-Universität
 Training mit Millionen von Kristalldaten zur Lösung kristallographischer Phasenprobleme, die Deep-Learning-Methode PhAI wird in Science veröffentlicht
Aug 08, 2024 pm 09:22 PM
Training mit Millionen von Kristalldaten zur Lösung kristallographischer Phasenprobleme, die Deep-Learning-Methode PhAI wird in Science veröffentlicht
Aug 08, 2024 pm 09:22 PM
Herausgeber |KX Bis heute sind die durch die Kristallographie ermittelten Strukturdetails und Präzision, von einfachen Metallen bis hin zu großen Membranproteinen, mit keiner anderen Methode zu erreichen. Die größte Herausforderung, das sogenannte Phasenproblem, bleibt jedoch die Gewinnung von Phaseninformationen aus experimentell bestimmten Amplituden. Forscher der Universität Kopenhagen in Dänemark haben eine Deep-Learning-Methode namens PhAI entwickelt, um Kristallphasenprobleme zu lösen. Ein Deep-Learning-Neuronales Netzwerk, das mithilfe von Millionen künstlicher Kristallstrukturen und den entsprechenden synthetischen Beugungsdaten trainiert wird, kann genaue Elektronendichtekarten erstellen. Die Studie zeigt, dass diese Deep-Learning-basierte Ab-initio-Strukturlösungsmethode das Phasenproblem mit einer Auflösung von nur 2 Angström lösen kann, was nur 10 bis 20 % der bei atomarer Auflösung verfügbaren Daten im Vergleich zur herkömmlichen Ab-initio-Berechnung entspricht
 Das NVIDIA-Dialogmodell ChatQA wurde auf Version 2.0 weiterentwickelt, wobei die angegebene Kontextlänge 128 KB beträgt
Jul 26, 2024 am 08:40 AM
Das NVIDIA-Dialogmodell ChatQA wurde auf Version 2.0 weiterentwickelt, wobei die angegebene Kontextlänge 128 KB beträgt
Jul 26, 2024 am 08:40 AM
Die offene LLM-Community ist eine Ära, in der hundert Blumen blühen und konkurrieren. Sie können Llama-3-70B-Instruct, QWen2-72B-Instruct, Nemotron-4-340B-Instruct, Mixtral-8x22BInstruct-v0.1 und viele andere sehen hervorragende Darsteller. Allerdings weisen offene Modelle im Vergleich zu den proprietären Großmodellen GPT-4-Turbo in vielen Bereichen noch erhebliche Lücken auf. Zusätzlich zu allgemeinen Modellen wurden einige offene Modelle entwickelt, die sich auf Schlüsselbereiche spezialisieren, wie etwa DeepSeek-Coder-V2 für Programmierung und Mathematik und InternVL für visuelle Sprachaufgaben.
 Google AI gewann die Silbermedaille der IMO Mathematical Olympiad, das mathematische Argumentationsmodell AlphaProof wurde eingeführt und Reinforcement Learning ist zurück
Jul 26, 2024 pm 02:40 PM
Google AI gewann die Silbermedaille der IMO Mathematical Olympiad, das mathematische Argumentationsmodell AlphaProof wurde eingeführt und Reinforcement Learning ist zurück
Jul 26, 2024 pm 02:40 PM
Für KI ist die Mathematikolympiade kein Problem mehr. Am Donnerstag hat die künstliche Intelligenz von Google DeepMind eine Meisterleistung vollbracht: Sie nutzte KI, um meiner Meinung nach die eigentliche Frage der diesjährigen Internationalen Mathematikolympiade zu lösen, und war nur einen Schritt davon entfernt, die Goldmedaille zu gewinnen. Der IMO-Wettbewerb, der gerade letzte Woche zu Ende ging, hatte sechs Fragen zu Algebra, Kombinatorik, Geometrie und Zahlentheorie. Das von Google vorgeschlagene hybride KI-System beantwortete vier Fragen richtig und erzielte 28 Punkte und erreichte damit die Silbermedaillenstufe. Anfang dieses Monats hatte der UCLA-Professor Terence Tao gerade die KI-Mathematische Olympiade (AIMO Progress Award) mit einem Millionenpreis gefördert. Unerwarteterweise hatte sich das Niveau der KI-Problemlösung vor Juli auf dieses Niveau verbessert. Beantworten Sie die Fragen meiner Meinung nach gleichzeitig. Am schwierigsten ist es meiner Meinung nach, da sie die längste Geschichte, den größten Umfang und die negativsten Fragen haben
 PRO |. Warum verdienen große Modelle, die auf MoE basieren, mehr Aufmerksamkeit?
Aug 07, 2024 pm 07:08 PM
PRO |. Warum verdienen große Modelle, die auf MoE basieren, mehr Aufmerksamkeit?
Aug 07, 2024 pm 07:08 PM
Im Jahr 2023 entwickeln sich fast alle Bereiche der KI in beispielloser Geschwindigkeit weiter. Gleichzeitig verschiebt die KI ständig die technologischen Grenzen wichtiger Bereiche wie der verkörperten Intelligenz und des autonomen Fahrens. Wird der Status von Transformer als Mainstream-Architektur großer KI-Modelle durch den multimodalen Trend erschüttert? Warum ist die Erforschung großer Modelle auf Basis der MoE-Architektur (Mixture of Experts) zu einem neuen Trend in der Branche geworden? Können Large Vision Models (LVM) ein neuer Durchbruch im allgemeinen Sehvermögen sein? ...Aus dem PRO-Mitglieder-Newsletter 2023 dieser Website, der in den letzten sechs Monaten veröffentlicht wurde, haben wir 10 spezielle Interpretationen ausgewählt, die eine detaillierte Analyse der technologischen Trends und industriellen Veränderungen in den oben genannten Bereichen bieten, um Ihnen dabei zu helfen, Ihre Ziele in der Zukunft zu erreichen Jahr vorbereitet sein. Diese Interpretation stammt aus Week50 2023
 Um ein neues wissenschaftliches und komplexes Frage-Antwort-Benchmark- und Bewertungssystem für große Modelle bereitzustellen, haben UNSW, Argonne, die University of Chicago und andere Institutionen gemeinsam das SciQAG-Framework eingeführt
Jul 25, 2024 am 06:42 AM
Um ein neues wissenschaftliches und komplexes Frage-Antwort-Benchmark- und Bewertungssystem für große Modelle bereitzustellen, haben UNSW, Argonne, die University of Chicago und andere Institutionen gemeinsam das SciQAG-Framework eingeführt
Jul 25, 2024 am 06:42 AM
Herausgeber | Der Frage-Antwort-Datensatz (QA) von ScienceAI spielt eine entscheidende Rolle bei der Förderung der Forschung zur Verarbeitung natürlicher Sprache (NLP). Hochwertige QS-Datensätze können nicht nur zur Feinabstimmung von Modellen verwendet werden, sondern auch effektiv die Fähigkeiten großer Sprachmodelle (LLMs) bewerten, insbesondere die Fähigkeit, wissenschaftliche Erkenntnisse zu verstehen und zu begründen. Obwohl es derzeit viele wissenschaftliche QS-Datensätze aus den Bereichen Medizin, Chemie, Biologie und anderen Bereichen gibt, weisen diese Datensätze immer noch einige Mängel auf. Erstens ist das Datenformular relativ einfach, die meisten davon sind Multiple-Choice-Fragen. Sie sind leicht auszuwerten, schränken jedoch den Antwortauswahlbereich des Modells ein und können die Fähigkeit des Modells zur Beantwortung wissenschaftlicher Fragen nicht vollständig testen. Im Gegensatz dazu offene Fragen und Antworten
 Die Genauigkeitsrate erreicht 60,8 %. Das auf Transformer basierende Modell zur Vorhersage der chemischen Retrosynthese wurde in der Unterzeitschrift „Nature' veröffentlicht
Aug 06, 2024 pm 07:34 PM
Die Genauigkeitsrate erreicht 60,8 %. Das auf Transformer basierende Modell zur Vorhersage der chemischen Retrosynthese wurde in der Unterzeitschrift „Nature' veröffentlicht
Aug 06, 2024 pm 07:34 PM
Herausgeber | KX-Retrosynthese ist eine entscheidende Aufgabe in der Arzneimittelforschung und organischen Synthese, und KI wird zunehmend eingesetzt, um den Prozess zu beschleunigen. Bestehende KI-Methoden weisen eine unbefriedigende Leistung und eine begrenzte Vielfalt auf. In der Praxis verursachen chemische Reaktionen häufig lokale molekulare Veränderungen mit erheblichen Überschneidungen zwischen Reaktanten und Produkten. Davon inspiriert schlug das Team von Hou Tingjun an der Zhejiang-Universität vor, die einstufige retrosynthetische Vorhersage als eine Aufgabe zur Bearbeitung molekularer Ketten neu zu definieren und dabei die Zielmolekülkette iterativ zu verfeinern, um Vorläuferverbindungen zu erzeugen. Außerdem wird ein bearbeitungsbasiertes retrosynthetisches Modell EditRetro vorgeschlagen, mit dem qualitativ hochwertige und vielfältige Vorhersagen erzielt werden können. Umfangreiche Experimente zeigen, dass das Modell beim Standard-Benchmark-Datensatz USPTO-50 K eine hervorragende Leistung mit einer Top-1-Genauigkeit von 60,8 % erzielt.