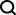Peranti teknologi
Peranti teknologi
 AI
AI
 Ringkasan perbandingan sepuluh teknik pengurangan dimensi tak linear dalam pembelajaran mesin
Ringkasan perbandingan sepuluh teknik pengurangan dimensi tak linear dalam pembelajaran mesin
Ringkasan perbandingan sepuluh teknik pengurangan dimensi tak linear dalam pembelajaran mesin
Pengurangan dimensi merujuk kepada mengekalkan maklumat utama data sebanyak mungkin sambil mengurangkan bilangan ciri dalam set data. Algoritma pengurangan dimensi ialah pembelajaran tanpa pengawasan, dan algoritma dilatih melalui data tidak berlabel.

Walaupun terdapat banyak jenis kaedah pengurangan dimensi, semuanya boleh dikelaskan kepada dua kategori utama: linear dan bukan linear.
Kaedah linear menayangkan data secara linear daripada ruang berdimensi tinggi kepada ruang berdimensi rendah (oleh itu dinamakan unjuran linear). Contohnya termasuk PCA dan LDA.
Kaedah tak linear ialah cara untuk melakukan pengurangan dimensi tak linear, selalunya digunakan untuk menemui struktur tak linear data asal. Kaedah pengurangan dimensi bukan linear amat penting apabila data asal tidak mudah dipisahkan secara linear. Dalam sesetengah kes, pengurangan dimensi tak linear juga dikenali sebagai pembelajaran manifold Kaedah ini boleh mengendalikan data berdimensi tinggi dengan lebih cekap dan membantu mendedahkan struktur asas data. Melalui pengurangan dimensi tak linear, kami dapat memahami dengan lebih baik hubungan antara data, menemui corak dan peraturan tersembunyi dalam data, dan memberikan sokongan padu untuk analisis dan aplikasi data selanjutnya.
Artikel ini telah menyusun 10 teknik pengurangan dimensi tak linear yang biasa digunakan untuk membantu anda memilih dalam kerja harian anda
1. Anda mungkin biasa dengan PCA biasa, iaitu teknik pengurangan dimensi linear. Kernel PCA boleh dilihat sebagai versi bukan linear analisis komponen utama biasa.
Kedua-dua analisis komponen utama dan analisis komponen utama kernel boleh digunakan untuk pengurangan dimensi, tetapi PCA kernel lebih berkesan dalam memproses data yang tidak boleh dipisahkan secara linear. Kelebihan utama kernel PCA adalah untuk mengubah data tidak boleh dipisahkan secara linear kepada data boleh dipisahkan secara linear sambil mengurangkan dimensi data. Kernel PCA boleh menangkap struktur tak linear dalam data dengan memperkenalkan teknik kernel, dengan itu meningkatkan prestasi klasifikasi data. Oleh itu, kernel PCA mempunyai kebolehan ekspresif dan generalisasi yang lebih kukuh apabila berurusan dengan set data yang kompleks.
Kami mula-mula mencipta data yang sangat klasik:
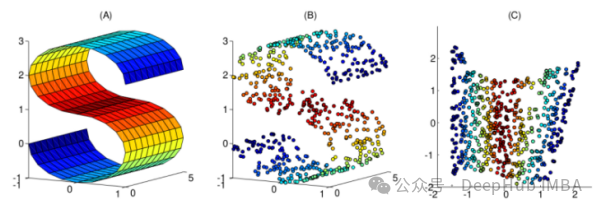
import matplotlib.pyplot as plt plt.figure(figsize=[7, 5]) from sklearn.datasets import make_moons X, y = make_moons(n_samples=100, noise=None, random_state=0) plt.scatter(X[:, 0], X[:, 1], c=y, s=50, cmap='plasma') plt.title('Linearly inseparable data')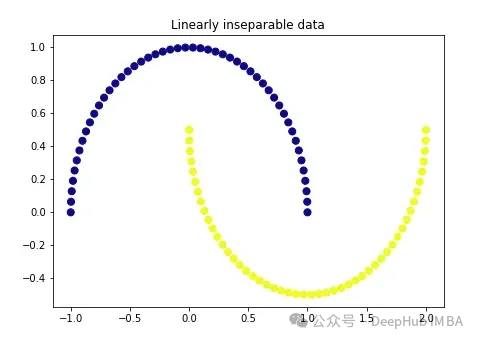 Dua warna ini mewakili dua kategori yang tidak boleh dipisahkan secara linear. Adalah mustahil untuk melukis garis lurus di sini untuk memisahkan kedua-dua kategori ini.
Dua warna ini mewakili dua kategori yang tidak boleh dipisahkan secara linear. Adalah mustahil untuk melukis garis lurus di sini untuk memisahkan kedua-dua kategori ini.
Kami bermula dengan PCA biasa.
import numpy as np from sklearn.decomposition import PCA pca = PCA(n_components=1) X_pca = pca.fit_transform(X) plt.figure(figsize=[7, 5]) plt.scatter(X_pca[:, 0], np.zeros((100,1)), c=y, s=50, cmap='plasma') plt.title('First component after linear PCA') plt.xlabel('PC1') Seperti yang anda lihat, kedua-dua kelas ini masih tidak boleh dipisahkan secara linear, sekarang mari cuba PCA kernel.
Seperti yang anda lihat, kedua-dua kelas ini masih tidak boleh dipisahkan secara linear, sekarang mari cuba PCA kernel.
import numpy as np from sklearn.decomposition import KernelPCA kpca = KernelPCA(n_components=1, kernel='rbf', gamma=15) X_kpca = kpca.fit_transform(X) plt.figure(figsize=[7, 5]) plt.scatter(X_kpca[:, 0], np.zeros((100,1)), c=y, s=50, cmap='plasma') plt.axvline(x=0.0, linestyle='dashed', color='black', linewidth=1.2) plt.title('First component after kernel PCA') plt.xlabel('PC1')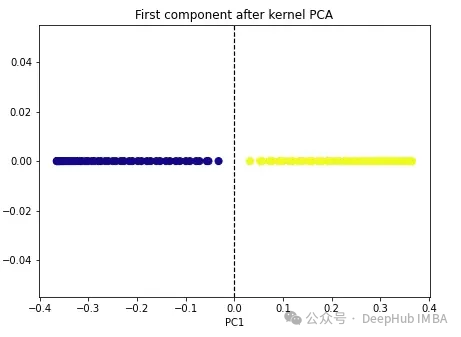 Kedua-dua kelas menjadi boleh dipisahkan secara linear, dan algoritma PCA kernel menggunakan kernel yang berbeza untuk mengubah data dari satu bentuk ke bentuk yang lain. Kernel PCA ialah proses dua langkah. Pertama, fungsi kernel menayangkan sementara data asal ke dalam ruang dimensi tinggi, di mana kelas boleh dipisahkan secara linear. Algoritma kemudian menayangkan data ini kembali ke dimensi yang lebih rendah yang dinyatakan dalam hiperparameter n_components (bilangan dimensi yang ingin kita simpan).
Kedua-dua kelas menjadi boleh dipisahkan secara linear, dan algoritma PCA kernel menggunakan kernel yang berbeza untuk mengubah data dari satu bentuk ke bentuk yang lain. Kernel PCA ialah proses dua langkah. Pertama, fungsi kernel menayangkan sementara data asal ke dalam ruang dimensi tinggi, di mana kelas boleh dipisahkan secara linear. Algoritma kemudian menayangkan data ini kembali ke dimensi yang lebih rendah yang dinyatakan dalam hiperparameter n_components (bilangan dimensi yang ingin kita simpan).
Terdapat empat pilihan kernel dalam sklearn: linear', 'poly', 'rbf' dan 'sigmoid'. Jika kita menentukan kernel sebagai "linear", PCA biasa akan dilakukan. Sebarang kernel lain akan melaksanakan PCA tak linear. Kernel rbf (fungsi asas jejari) adalah yang paling biasa digunakan.
2. Penskalaan berbilang dimensi (MDS)
Penskalaan berbilang dimensi ialah satu lagi teknik pengurangan dimensi bukan linear yang melakukan pengurangan dimensi dengan mengekalkan jarak antara titik data berdimensi tinggi dan rendah. Sebagai contoh, titik yang lebih dekat dalam dimensi asal juga kelihatan lebih dekat dalam dimensi yang lebih rendah.
Untuk melakukan ini dalam Scikit-lear kita boleh menggunakan kelas MDS().
from sklearn.manifold import MDS mds = MDS(n_components, metric) mds_transformed = mds.fit_transform(X)
Kami menggunakan dua jenis algoritma MDS pada data tak linear berikut.
import numpy as np from sklearn.manifold import MDS mds = MDS(n_components=1, metric=True) # Metric MDS X_mds = mds.fit_transform(X) plt.figure(figsize=[7, 5]) plt.scatter(X_mds[:, 0], np.zeros((100,1)), c=y, s=50, cmap='plasma') plt.title('Metric MDS') plt.xlabel('Component 1')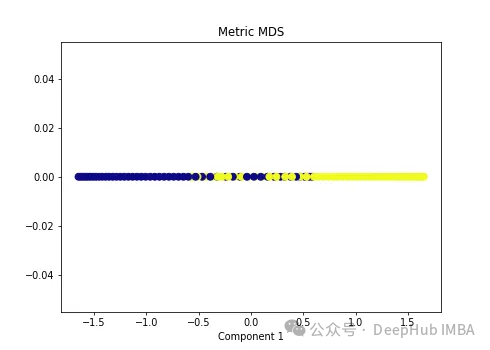
import numpy as np from sklearn.manifold import MDS mds = MDS(n_components=1, metric=False) # Non-metric MDS X_mds = mds.fit_transform(X) plt.figure(figsize=[7, 5]) plt.scatter(X_mds[:, 0], np.zeros((100,1)), c=y, s=50, cmap='plasma') plt.title('Non-metric MDS') plt.xlabel('Component 1')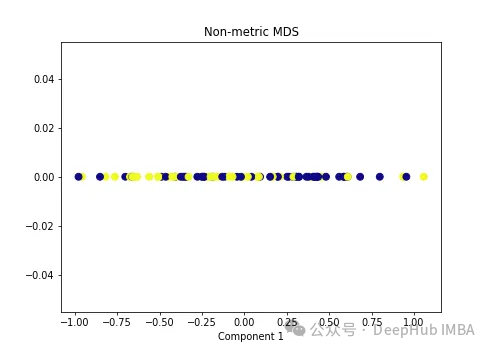
可以看到MDS后都不能使数据线性可分,所以可以说MDS不适合我们这个经典的数据集。
3、Isomap
Isomap(Isometric Mapping)在保持数据点之间的地理距离,即在原始高维空间中的测地线距离或者近似的测地线距离,在低维空间中也被保持。Isomap的基本思想是通过在高维空间中计算数据点之间的测地线距离(通过最短路径算法,比如Dijkstra算法),然后在低维空间中保持这些距离来进行降维。在这个过程中,Isomap利用了流形假设,即假设高维数据分布在一个低维流形上。因此,Isomap通常在处理非线性数据集时表现良好,尤其是当数据集包含曲线和流形结构时。
import matplotlib.pyplot as plt plt.figure(figsize=[7, 5]) from sklearn.datasets import make_moons X, y = make_moons(n_samples=100, noise=None, random_state=0) import numpy as np from sklearn.manifold import Isomap isomap = Isomap(n_neighbors=5, n_components=1) X_isomap = isomap.fit_transform(X) plt.figure(figsize=[7, 5]) plt.scatter(X_isomap[:, 0], np.zeros((100,1)), c=y, s=50, cmap='plasma') plt.title('First component after applying Isomap') plt.xlabel('Component 1')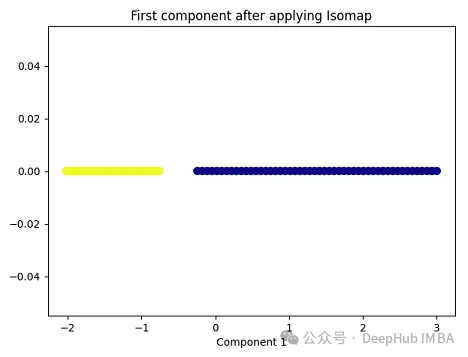
就像核PCA一样,这两个类在应用Isomap后是线性可分的!
4、Locally Linear Embedding(LLE)
与Isomap类似,LLE也是基于流形假设,即假设高维数据分布在一个低维流形上。LLE的主要思想是在局部邻域内保持数据点之间的线性关系,并在低维空间中重构这些关系。
from sklearn.manifold import LocallyLinearEmbedding lle = LocallyLinearEmbedding(n_neighbors=5,n_components=1) lle_transformed = lle.fit_transform(X) plt.figure(figsize=[7, 5]) plt.scatter(lle_transformed[:, 0], np.zeros((100,1)), c=y, s=50, cmap='plasma') plt.title('First component after applying LocallyLinearEmbedding') plt.xlabel('Component 1')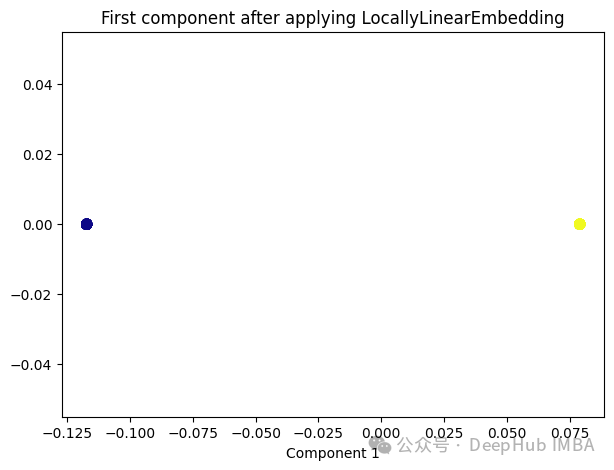
只有2个点,其实并不是这样,我们打印下这个数据
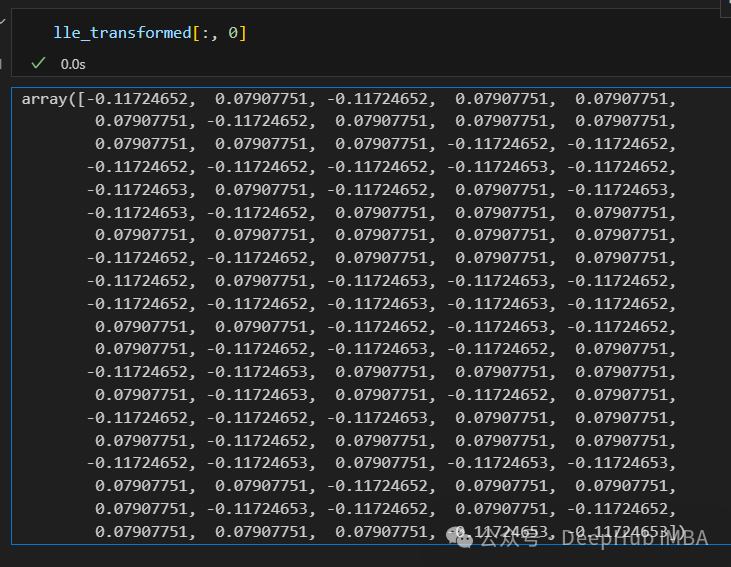
可以看到数据通过降维变成了同一个数字,所以LLE降维后是线性可分的,但是却丢失了数据的信息。
5、Spectral Embedding
Spectral Embedding是一种基于图论和谱理论的降维技术,通常用于将高维数据映射到低维空间。它的核心思想是利用数据的相似性结构,将数据点表示为图的节点,并通过图的谱分解来获取低维表示。
from sklearn.manifold import SpectralEmbedding sp_emb = SpectralEmbedding(n_components=1, affinity='nearest_neighbors') sp_emb_transformed = sp_emb.fit_transform(X) plt.figure(figsize=[7, 5]) plt.scatter(sp_emb_transformed[:, 0], np.zeros((100,1)), c=y, s=50, cmap='plasma') plt.title('First component after applying SpectralEmbedding') plt.xlabel('Component 1')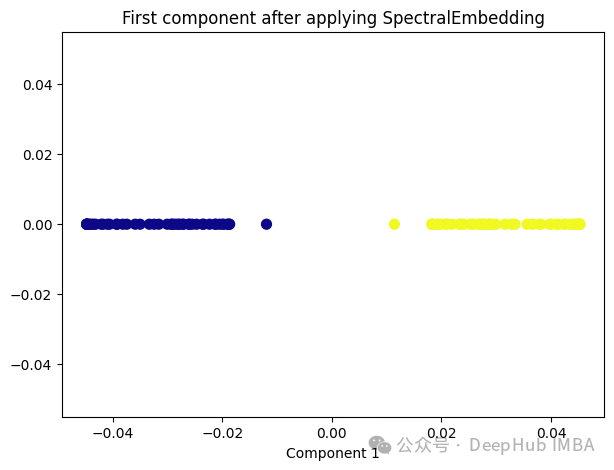
6、t-Distributed Stochastic Neighbor Embedding (t-SNE)
t-SNE的主要目标是保持数据点之间的局部相似性关系,并在低维空间中保持这些关系,同时试图保持全局结构。
from sklearn.manifold import TSNE tsne = TSNE(1, learning_rate='auto', init='pca') tsne_transformed = tsne.fit_transform(X) plt.figure(figsize=[7, 5]) plt.scatter(tsne_transformed[:, 0], np.zeros((100,1)), c=y, s=50, cmap='plasma') plt.title('First component after applying TSNE') plt.xlabel('Component 1')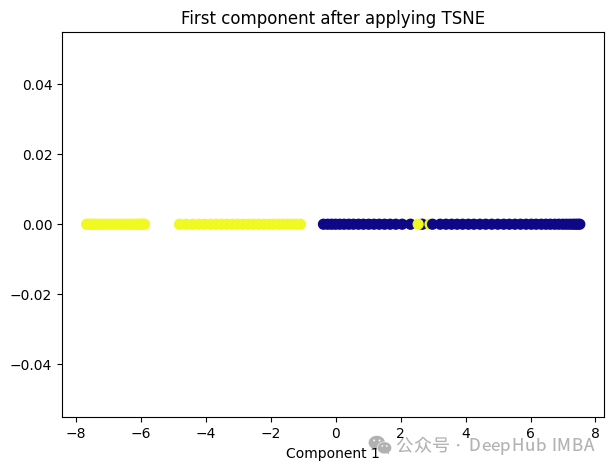
t-SNE好像也不太适合我们的数据。
7、Random Trees Embedding
Random Trees Embedding是一种基于树的降维技术,常用于将高维数据映射到低维空间。它利用了随机森林(Random Forest)的思想,通过构建多棵随机决策树来实现降维。
Random Trees Embedding的基本工作流程:
- 构建随机决策树集合:首先,构建多棵随机决策树。每棵树都是通过从原始数据中随机选择子集进行训练的,这样可以减少过拟合,提高泛化能力。
- 提取特征表示:对于每个数据点,通过将其在每棵树上的叶子节点的索引作为特征,构建一个特征向量。每个叶子节点都代表了数据点在树的某个分支上的位置。
- 降维:通过随机森林中所有树生成的特征向量,将数据点映射到低维空间中。通常使用降维技术,如主成分分析(PCA)或t-SNE等,来实现最终的降维过程。
Random Trees Embedding的优势在于它的计算效率高,特别是对于大规模数据集。由于使用了随机森林的思想,它能够很好地处理高维数据,并且不需要太多的调参过程。
RandomTreesEmbedding使用高维稀疏进行无监督转换,也就是说,我们最终得到的数据并不是一个连续的数值,而是稀疏的表示。所以这里就不进行代码展示了,有兴趣的看看sklearn的sklearn.ensemble.RandomTreesEmbedding
8、Dictionary Learning
Dictionary Learning是一种用于降维和特征提取的技术,它主要用于处理高维数据。它的目标是学习一个字典,该字典由一组原子(或基向量)组成,这些原子是数据的线性组合。通过学习这样的字典,可以将高维数据表示为一个更紧凑的低维空间中的稀疏线性组合。
Dictionary Learning的优点之一是它能够学习出具有可解释性的原子,这些原子可以提供关于数据结构和特征的重要见解。此外,Dictionary Learning还可以产生稀疏表示,从而提供更紧凑的数据表示,有助于降低存储成本和计算复杂度。
from sklearn.decomposition import DictionaryLearning dict_lr = DictionaryLearning(n_components=1) dict_lr_transformed = dict_lr.fit_transform(X) plt.figure(figsize=[7, 5]) plt.scatter(dict_lr_transformed[:, 0], np.zeros((100,1)), c=y, s=50, cmap='plasma') plt.title('First component after applying DictionaryLearning') plt.xlabel('Component 1')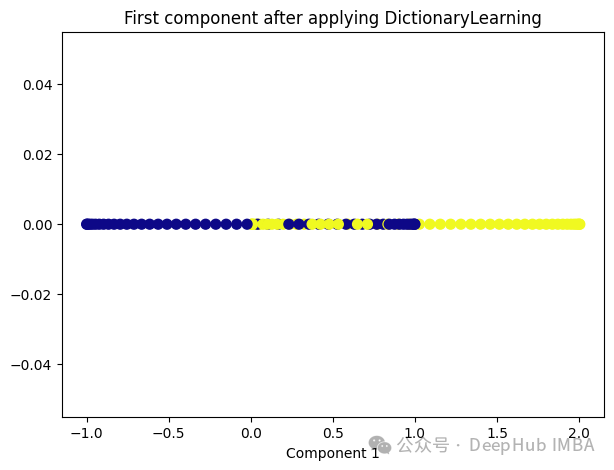
9、Independent Component Analysis (ICA)
Independent Component Analysis (ICA) 是一种用于盲源分离的统计方法,通常用于从混合信号中估计原始信号。在机器学习和信号处理领域,ICA经常用于解决以下问题:
- 盲源分离:给定一组混合信号,其中每个信号是一组原始信号的线性组合,ICA的目标是从混合信号中分离出原始信号,而不需要事先知道混合过程的具体细节。
- 特征提取:ICA可以被用来发现数据中的独立成分,提取数据的潜在结构和特征,通常在降维或预处理过程中使用。
ICA的基本假设是,混合信号中的各个成分是相互独立的,即它们的统计特性是独立的。这与主成分分析(PCA)不同,PCA假设成分之间是正交的,而不是独立的。因此ICA通常比PCA更适用于发现非高斯分布的独立成分。
from sklearn.decomposition import FastICA ica = FastICA(n_components=1, whiten='unit-variance') ica_transformed = dict_lr.fit_transform(X) plt.figure(figsize=[7, 5]) plt.scatter(ica_transformed[:, 0], np.zeros((100,1)), c=y, s=50, cmap='plasma') plt.title('First component after applying FastICA') plt.xlabel('Component 1')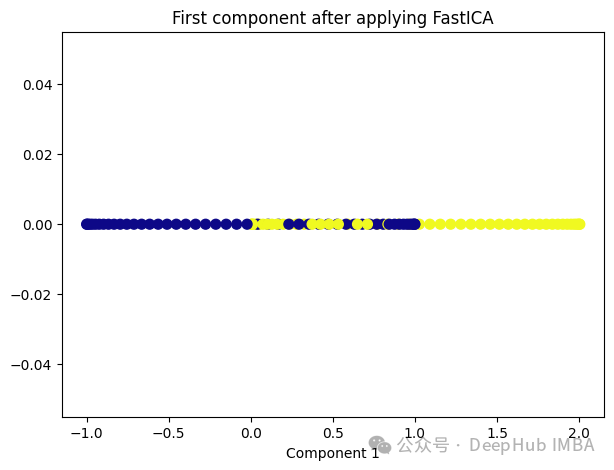
10、Autoencoders (AEs)
到目前为止,我们讨论的NLDR技术属于通用机器学习算法的范畴。而自编码器是一种基于神经网络的NLDR技术,可以很好地处理大型非线性数据。当数据集较小时,自动编码器的效果可能不是很好。
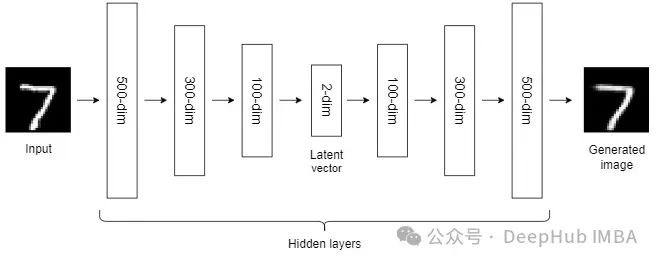
自编码器我们已经介绍过很多次了,所以这里就不详细说明了。
总结
非线性降维技术是一类用于将高维数据映射到低维空间的方法,它们通常适用于数据具有非线性结构的情况。
大多数NLDR方法基于最近邻方法,该方法要求数据中所有特征的尺度相同,所以如果特征的尺度不同,还需要进行缩放。
另外这些非线性降维技术在不同的数据集和任务中可能表现出不同的性能,因此在选择合适的方法时需要考虑数据的特征、降维的目标以及计算资源等因素。
Atas ialah kandungan terperinci Ringkasan perbandingan sepuluh teknik pengurangan dimensi tak linear dalam pembelajaran mesin. Untuk maklumat lanjut, sila ikut artikel berkaitan lain di laman web China PHP!

Alat AI Hot
Undresser.AI Undress
Apl berkuasa AI untuk mencipta foto bogel yang realistik
AI Clothes Remover
Alat AI dalam talian untuk mengeluarkan pakaian daripada foto.

Undress AI Tool
Gambar buka pakaian secara percuma

Clothoff.io
Penyingkiran pakaian AI

AI Hentai Generator
Menjana ai hentai secara percuma.

Artikel Panas

Alat panas

Notepad++7.3.1
Editor kod yang mudah digunakan dan percuma

SublimeText3 versi Cina
Versi Cina, sangat mudah digunakan

Hantar Studio 13.0.1
Persekitaran pembangunan bersepadu PHP yang berkuasa

Dreamweaver CS6
Alat pembangunan web visual

SublimeText3 versi Mac
Perisian penyuntingan kod peringkat Tuhan (SublimeText3)

Topik panas
 1384
1384
 52
52
 15 alat anotasi imej percuma sumber terbuka disyorkan
Mar 28, 2024 pm 01:21 PM
15 alat anotasi imej percuma sumber terbuka disyorkan
Mar 28, 2024 pm 01:21 PM
Anotasi imej ialah proses mengaitkan label atau maklumat deskriptif dengan imej untuk memberi makna dan penjelasan yang lebih mendalam kepada kandungan imej. Proses ini penting untuk pembelajaran mesin, yang membantu melatih model penglihatan untuk mengenal pasti elemen individu dalam imej dengan lebih tepat. Dengan menambahkan anotasi pada imej, komputer boleh memahami semantik dan konteks di sebalik imej, dengan itu meningkatkan keupayaan untuk memahami dan menganalisis kandungan imej. Anotasi imej mempunyai pelbagai aplikasi, meliputi banyak bidang, seperti penglihatan komputer, pemprosesan bahasa semula jadi dan model penglihatan graf Ia mempunyai pelbagai aplikasi, seperti membantu kenderaan dalam mengenal pasti halangan di jalan raya, dan membantu dalam proses. pengesanan dan diagnosis penyakit melalui pengecaman imej perubatan. Artikel ini terutamanya mengesyorkan beberapa alat anotasi imej sumber terbuka dan percuma yang lebih baik. 1.Makesen
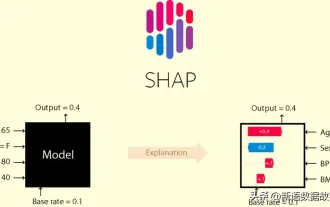 Artikel ini akan membawa anda memahami SHAP: penjelasan model untuk pembelajaran mesin
Jun 01, 2024 am 10:58 AM
Artikel ini akan membawa anda memahami SHAP: penjelasan model untuk pembelajaran mesin
Jun 01, 2024 am 10:58 AM
Dalam bidang pembelajaran mesin dan sains data, kebolehtafsiran model sentiasa menjadi tumpuan penyelidik dan pengamal. Dengan aplikasi meluas model yang kompleks seperti kaedah pembelajaran mendalam dan ensemble, memahami proses membuat keputusan model menjadi sangat penting. AI|XAI yang boleh dijelaskan membantu membina kepercayaan dan keyakinan dalam model pembelajaran mesin dengan meningkatkan ketelusan model. Meningkatkan ketelusan model boleh dicapai melalui kaedah seperti penggunaan meluas pelbagai model yang kompleks, serta proses membuat keputusan yang digunakan untuk menerangkan model. Kaedah ini termasuk analisis kepentingan ciri, anggaran selang ramalan model, algoritma kebolehtafsiran tempatan, dsb. Analisis kepentingan ciri boleh menerangkan proses membuat keputusan model dengan menilai tahap pengaruh model ke atas ciri input. Anggaran selang ramalan model
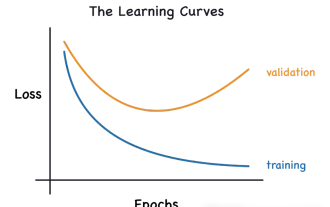 Kenal pasti overfitting dan underfitting melalui lengkung pembelajaran
Apr 29, 2024 pm 06:50 PM
Kenal pasti overfitting dan underfitting melalui lengkung pembelajaran
Apr 29, 2024 pm 06:50 PM
Artikel ini akan memperkenalkan cara mengenal pasti pemasangan lampau dan kekurangan dalam model pembelajaran mesin secara berkesan melalui keluk pembelajaran. Underfitting dan overfitting 1. Overfitting Jika model terlampau latihan pada data sehingga ia mempelajari bunyi daripadanya, maka model tersebut dikatakan overfitting. Model yang dipasang terlebih dahulu mempelajari setiap contoh dengan sempurna sehingga ia akan salah mengklasifikasikan contoh yang tidak kelihatan/baharu. Untuk model terlampau, kami akan mendapat skor set latihan yang sempurna/hampir sempurna dan set pengesahan/skor ujian yang teruk. Diubah suai sedikit: "Punca overfitting: Gunakan model yang kompleks untuk menyelesaikan masalah mudah dan mengekstrak bunyi daripada data. Kerana set data kecil sebagai set latihan mungkin tidak mewakili perwakilan yang betul bagi semua data. 2. Underfitting Heru
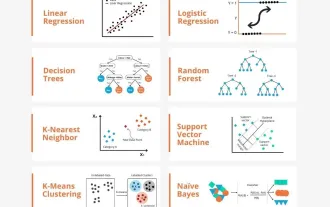 Telus! Analisis mendalam tentang prinsip model pembelajaran mesin utama!
Apr 12, 2024 pm 05:55 PM
Telus! Analisis mendalam tentang prinsip model pembelajaran mesin utama!
Apr 12, 2024 pm 05:55 PM
Dalam istilah orang awam, model pembelajaran mesin ialah fungsi matematik yang memetakan data input kepada output yang diramalkan. Secara lebih khusus, model pembelajaran mesin ialah fungsi matematik yang melaraskan parameter model dengan belajar daripada data latihan untuk meminimumkan ralat antara output yang diramalkan dan label sebenar. Terdapat banyak model dalam pembelajaran mesin, seperti model regresi logistik, model pepohon keputusan, model mesin vektor sokongan, dll. Setiap model mempunyai jenis data dan jenis masalah yang berkenaan. Pada masa yang sama, terdapat banyak persamaan antara model yang berbeza, atau terdapat laluan tersembunyi untuk evolusi model. Mengambil perceptron penyambung sebagai contoh, dengan meningkatkan bilangan lapisan tersembunyi perceptron, kita boleh mengubahnya menjadi rangkaian neural yang mendalam. Jika fungsi kernel ditambah pada perceptron, ia boleh ditukar menjadi SVM. yang ini
 Evolusi kecerdasan buatan dalam penerokaan angkasa lepas dan kejuruteraan penempatan manusia
Apr 29, 2024 pm 03:25 PM
Evolusi kecerdasan buatan dalam penerokaan angkasa lepas dan kejuruteraan penempatan manusia
Apr 29, 2024 pm 03:25 PM
Pada tahun 1950-an, kecerdasan buatan (AI) dilahirkan. Ketika itulah penyelidik mendapati bahawa mesin boleh melakukan tugas seperti manusia, seperti berfikir. Kemudian, pada tahun 1960-an, Jabatan Pertahanan A.S. membiayai kecerdasan buatan dan menubuhkan makmal untuk pembangunan selanjutnya. Penyelidik sedang mencari aplikasi untuk kecerdasan buatan dalam banyak bidang, seperti penerokaan angkasa lepas dan kelangsungan hidup dalam persekitaran yang melampau. Penerokaan angkasa lepas ialah kajian tentang alam semesta, yang meliputi seluruh alam semesta di luar bumi. Angkasa lepas diklasifikasikan sebagai persekitaran yang melampau kerana keadaannya berbeza daripada di Bumi. Untuk terus hidup di angkasa, banyak faktor mesti dipertimbangkan dan langkah berjaga-jaga mesti diambil. Para saintis dan penyelidik percaya bahawa meneroka ruang dan memahami keadaan semasa segala-galanya boleh membantu memahami cara alam semesta berfungsi dan bersedia untuk menghadapi kemungkinan krisis alam sekitar
 Melaksanakan Algoritma Pembelajaran Mesin dalam C++: Cabaran dan Penyelesaian Biasa
Jun 03, 2024 pm 01:25 PM
Melaksanakan Algoritma Pembelajaran Mesin dalam C++: Cabaran dan Penyelesaian Biasa
Jun 03, 2024 pm 01:25 PM
Cabaran biasa yang dihadapi oleh algoritma pembelajaran mesin dalam C++ termasuk pengurusan memori, multi-threading, pengoptimuman prestasi dan kebolehselenggaraan. Penyelesaian termasuk menggunakan penunjuk pintar, perpustakaan benang moden, arahan SIMD dan perpustakaan pihak ketiga, serta mengikuti garis panduan gaya pengekodan dan menggunakan alat automasi. Kes praktikal menunjukkan cara menggunakan perpustakaan Eigen untuk melaksanakan algoritma regresi linear, mengurus memori dengan berkesan dan menggunakan operasi matriks berprestasi tinggi.
 Lima sekolah pembelajaran mesin yang anda tidak tahu
Jun 05, 2024 pm 08:51 PM
Lima sekolah pembelajaran mesin yang anda tidak tahu
Jun 05, 2024 pm 08:51 PM
Pembelajaran mesin ialah cabang penting kecerdasan buatan yang memberikan komputer keupayaan untuk belajar daripada data dan meningkatkan keupayaan mereka tanpa diprogramkan secara eksplisit. Pembelajaran mesin mempunyai pelbagai aplikasi dalam pelbagai bidang, daripada pengecaman imej dan pemprosesan bahasa semula jadi kepada sistem pengesyoran dan pengesanan penipuan, dan ia mengubah cara hidup kita. Terdapat banyak kaedah dan teori yang berbeza dalam bidang pembelajaran mesin, antaranya lima kaedah yang paling berpengaruh dipanggil "Lima Sekolah Pembelajaran Mesin". Lima sekolah utama ialah sekolah simbolik, sekolah sambungan, sekolah evolusi, sekolah Bayesian dan sekolah analogi. 1. Simbolisme, juga dikenali sebagai simbolisme, menekankan penggunaan simbol untuk penaakulan logik dan ekspresi pengetahuan. Aliran pemikiran ini percaya bahawa pembelajaran adalah proses penolakan terbalik, melalui sedia ada
 AI yang boleh dijelaskan: Menerangkan model AI/ML yang kompleks
Jun 03, 2024 pm 10:08 PM
AI yang boleh dijelaskan: Menerangkan model AI/ML yang kompleks
Jun 03, 2024 pm 10:08 PM
Penterjemah |. Disemak oleh Li Rui |. Chonglou Model kecerdasan buatan (AI) dan pembelajaran mesin (ML) semakin kompleks hari ini, dan output yang dihasilkan oleh model ini adalah kotak hitam – tidak dapat dijelaskan kepada pihak berkepentingan. AI Boleh Dijelaskan (XAI) bertujuan untuk menyelesaikan masalah ini dengan membolehkan pihak berkepentingan memahami cara model ini berfungsi, memastikan mereka memahami cara model ini sebenarnya membuat keputusan, dan memastikan ketelusan dalam sistem AI, Amanah dan akauntabiliti untuk menyelesaikan masalah ini. Artikel ini meneroka pelbagai teknik kecerdasan buatan (XAI) yang boleh dijelaskan untuk menggambarkan prinsip asasnya. Beberapa sebab mengapa AI boleh dijelaskan adalah penting Kepercayaan dan ketelusan: Untuk sistem AI diterima secara meluas dan dipercayai, pengguna perlu memahami cara keputusan dibuat